对抗知识焦虑,从看懂这条开始
App 下载
植物藏了4亿年的开关,现在能帮我们种好粮
基因调控|植物基因组|基因开关|保守非编码序列|基因组学|生命科学
对抗知识焦虑,从看懂这条开始
App 下载
基因调控|植物基因组|基因开关|保守非编码序列|基因组学|生命科学
你或许听过深海、深空,但未必听过“深时”——那是地质时间尺度里的亿年刻度,比人类文明长了几千倍。最近,一群科学家在314个植物基因组里,揪出了2.3百万个藏了4亿年的“基因开关”——保守非编码序列(CNSs),它们不编码蛋白质,却像隐形的钟表,精准控制着植物什么时候长叶、什么时候开花。
过去几十年,生物学家一直困惑:为啥不同植物的核心基因功能差不离,调控基因的“开关”却好像毫无章法?有人甚至断言,植物的调控DNA根本留不住4亿年。
这个假设错了。
要理解这些“开关”有多难发现,得先搞懂一个常识:植物的基因组像被揉过的草稿纸——亿万年里,它们不断复制基因、打乱染色体顺序,那些不编码蛋白质的调控序列,早就被埋进了杂乱的“草稿”里。传统方法只能盯着基因附近的一小片区域,自然看不到这些被打散的古老开关。
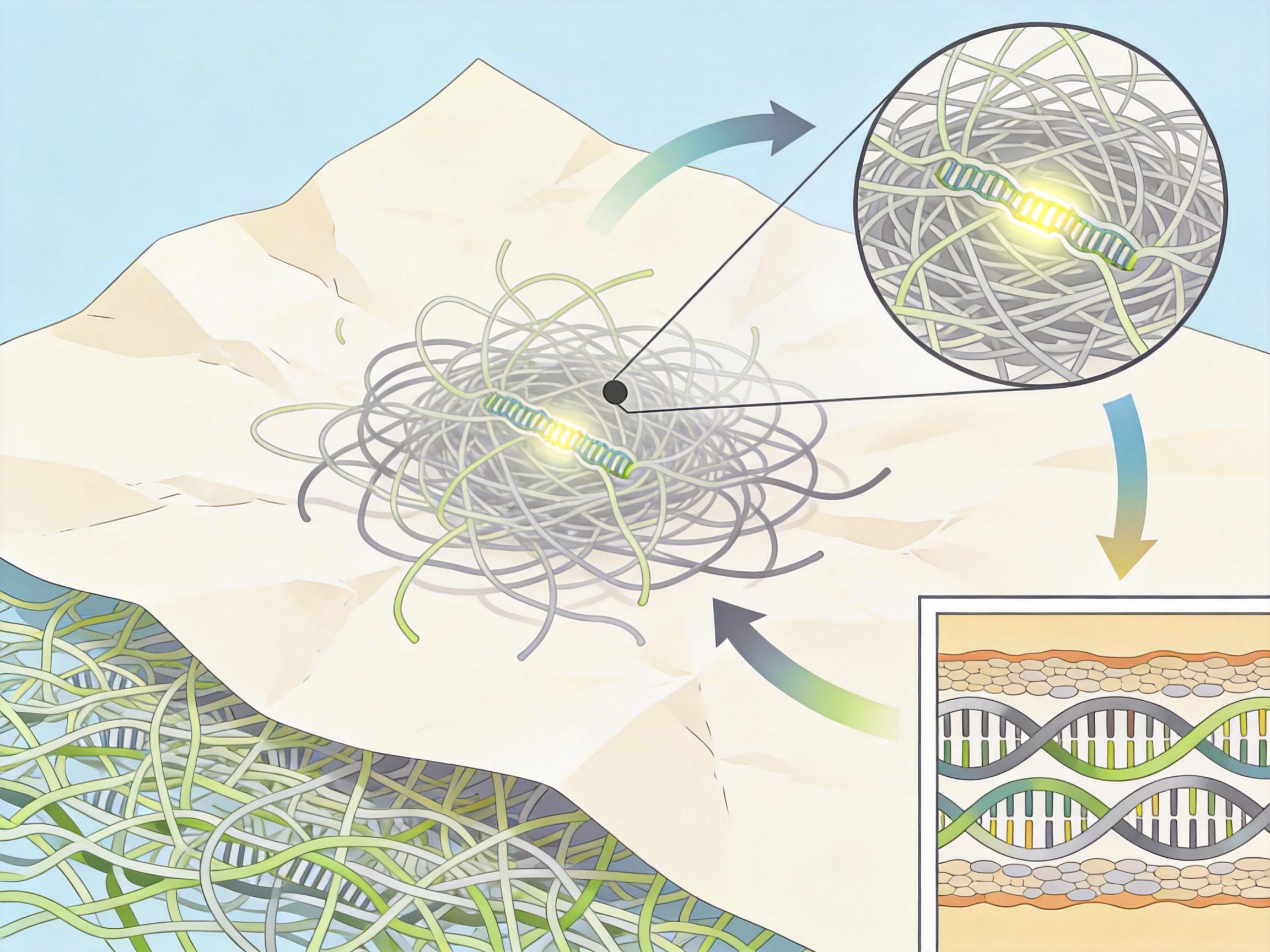
冷泉港实验室的团队联合全球合作者,搞出了个叫Conservatory的计算工具——你可以把它想象成一个能拼碎纸的AI,它不看单个基因,而是盯着“基因簇”的排列模式:比如三个基因在苔藓里是ABC顺序,到了水稻里变成了A__B_C(空格代表插入的新序列),它就能把中间的空格忽略,认出这三个基因的原始关联,进而揪出藏在附近的CNS。
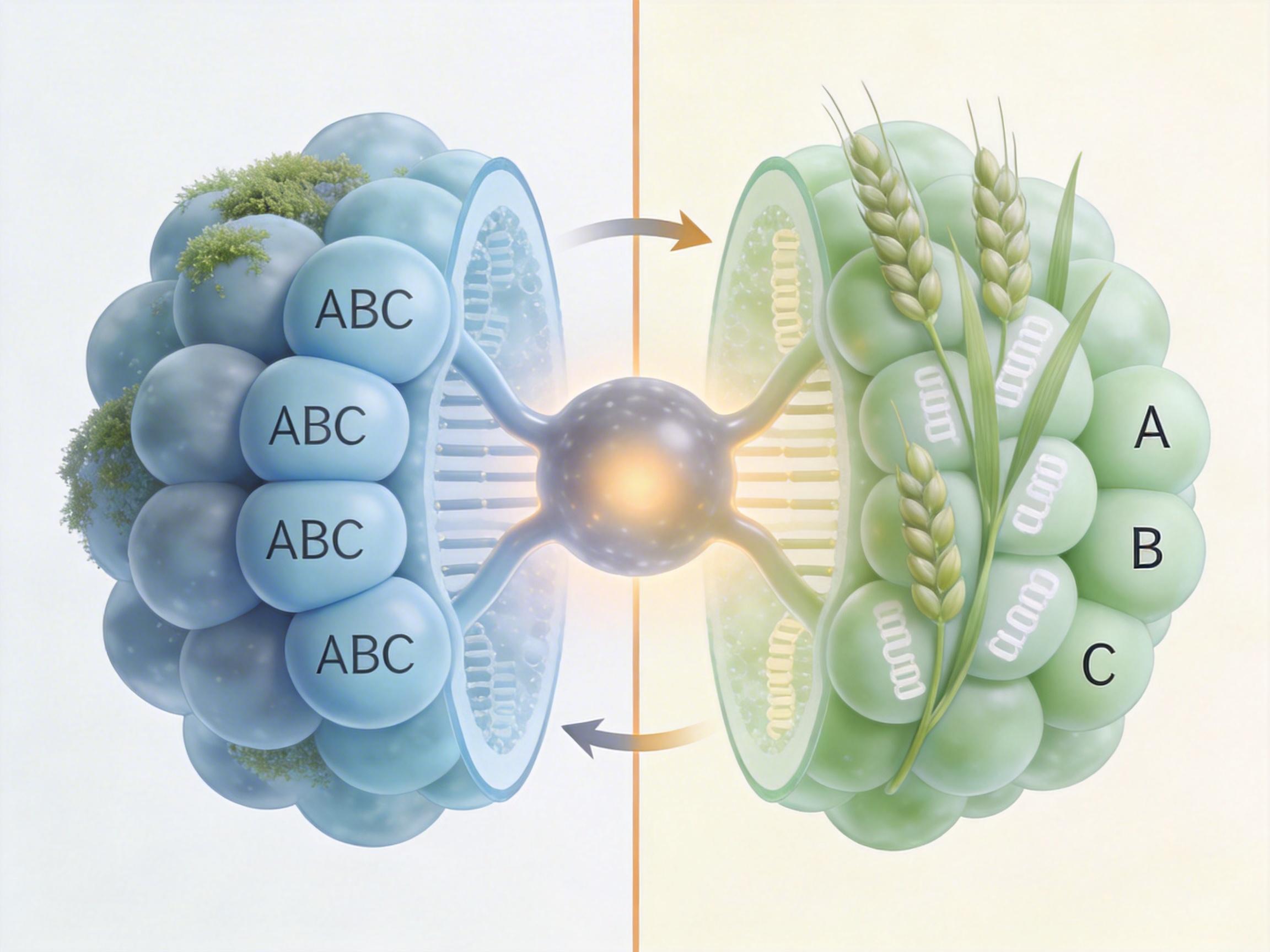
这个工具一出手就炸出了2.3百万个CNS,其中3000多个能追溯到4亿年前——那时候,开花植物还没从蕨类和苔藓里分化出来。更关键的是,他们用CRISPR编辑了几个古老CNS,比如控制茎尖干细胞的WUS基因附近的序列,结果植物直接长歪了,证明这些开关是真的在干活,不是没用的“垃圾DNA”。
这些CNS能活过4亿年,靠的不是“一动不动”,而是一套灵活的生存法则。团队总结出了三条:
第一,顺序比位置重要。比如两个CNS在苔藓里是紧挨着的AB,到了小麦里可能被插到了不同的染色体区域,但只要还是AB的顺序,它们就能一起调控同一个基因。就像两个搭档,哪怕换了办公室,只要分工不变,就能接着干活。
第二,能换“老板”。基因组重排的时候,CNS可能会从一个基因旁边跑到另一个基因旁边,和新的基因形成调控关系。这就像一个HR,换了公司还是能做招聘,只是服务的老板变了。
第三,复制后留备份。植物经常会整个基因组复制,这时候古老的CNS会被保留下来,其中一份继续干老本行,另一份慢慢变异成新的开关——这就是植物进化出不同形态的关键:比如从苔藓的扁平叶,到被子植物的复杂花型,可能就是老开关变异出了新功能。
我认为,这是最被低估的发现:过去我们总觉得进化是“淘汰旧的,创造新的”,但植物的调控系统是“留着老的,改出新的”——4亿年的“库存”,成了它们适应环境的最大资本。
这些藏了4亿年的开关,现在轮到人类用了。过去我们改良作物,要么靠杂交碰运气,要么直接敲掉某个基因——就像把家里的灯直接拆了,要么全亮要么全灭。但CNS不一样,它是调节亮度的旋钮。
比如玉米里的ARGOS8基因,它能提高抗旱性,但直接过表达会让玉米长得太矮。现在我们可以编辑它附近的CNS,让它只在干旱的时候启动,既抗旱又不影响产量。再比如水稻的OsSWEET基因,细菌会通过它的启动子入侵,我们只要删掉启动子里的一个CNS,就能让水稻抗病,又不影响正常生长。
更妙的是,这些CNS是跨物种保守的:比如苔藓里控制根发育的开关,可能在小麦里也能用。这意味着我们可以从4亿年的植物“基因库”里找工具,不用再从零开始试错。不过有个盲区得提:现在我们还不知道每个CNS具体管什么,大部分编辑还是靠试——就像拿到了一堆旋钮,却不知道哪个管亮度哪个管颜色。
当我们盯着实验室里的水稻和小麦时,其实是在和4亿年前的植物祖先对话。那些藏在基因组里的开关,见证了蕨类登陆、被子植物开花,也见证了冰川融化、气候剧变。
“古老的秩序,是未来的底气。”这句话放在这里再合适不过——我们总在追求“新”的技术、“新”的品种,却忘了大自然已经在4亿年里,给我们留下了最靠谱的“用户手册”。
下一次你吃一口米饭,或许可以想想:这粒米的生长,可能被一个4亿年前就存在的开关,悄悄调控着。